清华大学生命学院颉伟团队合作揭示H3K36me2重编程调控哺乳动物胚胎着床后DNA甲基化重建的机制
2025/12/05
DNA甲基化在基因表达、基因印记和X染色体失活等过程中发挥着重要的调控功能。作为细胞表观记忆机制的重要组成部分,DNA甲基化在体细胞分裂中能够稳定遗传。然而,在哺乳动物配子发生和早期胚胎发育过程中,DNA甲基化经历了广泛而剧烈的重编程,以完成亲代-子代转变和发育时钟的重置。在哺乳动物的整个生命周期中,DNA甲基化经历了三次大规模的重新建立过程,分别发生于精子发生、卵子发生和胚胎着床之后。其中,精子发生和卵子发生阶段的DNA甲基化建立分别受组蛋白修饰H3K36me2和H3K36me3严格调控,但胚胎着床后DNA甲基化重建的分子机制仍不清楚。
11月11日,清华大学生命科学学院颉伟教授团队、山东大学妇儿与生殖健康研究院卢绪坤副研究员团队和复旦大学生殖与发育研究院张宇研究员团队合作,在《自然·细胞生物学》(Nature Cell Biology)发表题为“H3K36me2重编程谱系特异性调控着床后DNA甲基化从头建立”(Reprogramming of H3K36me2 guides lineage-specific post-implantation de novo DNA methylation)的研究论文。研究通过系统检测小鼠早期胚胎发育过程中H3K36me2的动态重编程,揭示了H3K36me2重编程协同DNMT3A/3B以谱系特异性的方式调控着床后DNA甲基化重建的功能和分子机制。
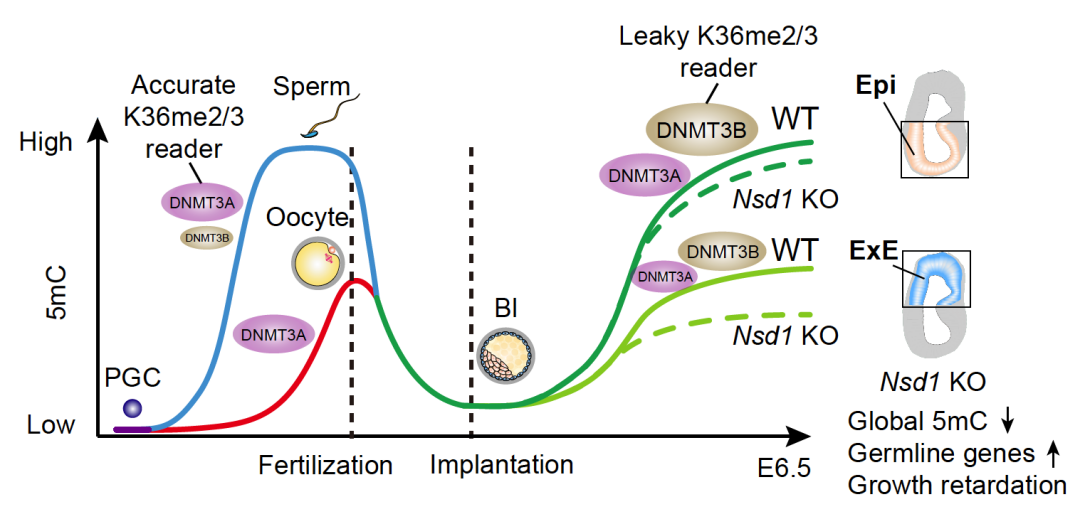
研究团队首先系统绘制了小鼠卵母细胞、着床前和着床后胚胎中的H3K36me2动态变化图谱,发现卵母细胞转录影响H3K36me2与H3K36me3之间的相互转变。在转录沉默的卵母细胞中,H3K36me2更倾向于定位到基因体(genebody)区域。受精之后,父本H3K36me2快速丢失,而母本H3K36me2在8-细胞之后丢失。合子基因组激活(Zygotic genome activation, ZGA)之后,H3K36me2呈现两步建立过程:着床前胚胎H3K36me2首先在增强子逐步建立(Seeding),着床后遍布大部分基因组(Spreading)(失活的X染色体除外)。
为研究H3K36me2在着床后DNA甲基化重建中的功能和对胚胎发育的影响,研究团队构建了H3K36me2甲基转移酶——NSD1酶活突变的小鼠模型。结果显示,H3K36me2缺失显著影响胚外组织中DNA甲基化的重建,但是对胚胎组织中DNA甲基化重建的影响较小。进一步研究表明,DNMT3A通过PWWP结构域严格识别和依赖H3K36me2/3(Accurate reader),而DNMT3B则可以不依赖H3K36me2/3进行DNA甲基化(Leaky reader)。因此,胚胎组织中高表达的DNMT3B在H3K36me2缺失的情况下仍可以保证全局性DNA甲基化的建立。但是,H3K36me2对于经常受到甲基化调控的启动子,包括生殖系特异性基因启动子的有效甲基化和沉默是必需的。研究还发现,富含发育关键基因的DMV(DNA methylation valley)区域能够通过PRC1/H2AK119ub1抑制H3K36me2,进而防止该区域被异常甲基化。
值得关注的是,在小鼠精子和卵子中,DNMT3B通常低表达甚至不表达,而DNMT3A是最重要的从头DNA甲基化酶,由于DNMT3A严格依赖H3K36me2/3,研究团队认为这种分工可能保证了基因印记(一种控制两性繁殖的亲本差异化DNA甲基化现象)能够在精卵中准确建立。
综上所述,研究揭示了H3K36me2在小鼠早期胚胎发育中的重编程规律,包括其两步建立过程,并确定了H3K36me2在着床后胚胎中谱系和位点特异性DNA甲基化重建及基因调控中的重要作用。此外,研究还解析了DNMT3A和DNMT3B在建立DNA甲基化时对H3K36me2/3的不同依赖性。研究不仅加深了对不同生物学过程中DNA甲基化建立调控机制的理解,也将为不孕不育的诊断治疗和更精准表观组编辑工具的开发提供理论依据。
H3K36me2协同DNMT3A/3B谱系特异性调控着床后DNA甲基化的重建
清华大学生命科学学院教授颉伟、山东大学妇儿与生殖健康研究院副研究员卢绪坤和复旦大学生殖与发育研究院研究员张宇为论文共同通讯作者。卢绪坤和清华大学生命科学学院2023级博士生王利娟为论文共同第一作者。
研究得到国家重点研发计划、国家自然科学基金、上海市自然科学基金、清华-北京生命科学中心、新基石基金的经费支持,同时得到清华大学实验动物中心、生物医学测试中心基因测序平台以及计算平台的大力协助和支持。
文章来源清华大学,分享只为学术交流,如涉及侵权问题请联系我们,我们将及时修改或删除。
-
2026年6月优质国际学术会议推荐 7

-
2026年第17届机械与航空航天工程 193

-
2026年先进航空航天技术与卫星应用 324

-
2026资源、化学化工与应用材料国际 1808

-
2026年图像处理与数字创意设计国际 1632

-
2026年机械工程,新能源与电气技术 6095

-
2026年材料科学、低碳技术与动力工 1819

-
2026年艺术、文化产业与数字媒体国 04-29

-
2026年智慧教育、教育研究与文化交 04-29

-
2026年数字社会、公共管理与经济学 04-29

-
2026 政务服务、数字治理与智慧城 04-28

-
2026 制冷技术、暖通设备与环境调 04-28

-
2026 轻工材料、绿色制造与循环利 04-28

-
2026 多语言智能、翻译技术与国际 04-28

-
2026 生物育种、生态种植与现代农 04-28

-
中国科协发布2025年《重要学术12

-
2026年新锐分区(原中科院期刊2595

-
2025年两院院士增选有效候选人4402

-
2025最新JCR分区及影响因子12342

-
好学术:科研网址导航|学术头条分5673

-
2025年国际期刊预警名单发布!5837

-
2025年中科院期刊分区表重磅发20812

-
吉林大学校长张希:学术会议中的提6954

-
二维超导迈斯纳效应探测研究获进展04-29

-
研究发现笼目超导体中多重范霍夫奇04-29

-
二氧化碳加氢制高碳烯烃与航煤馏分04-29

-
靶向特定蛋白互作界面抑制乙肝病毒04-29

-
研究揭示内源信使调控膜损伤与细胞04-29

-
科学家绘制大脑星形胶质细胞转录因04-29

-
上海交大Bio-X研究院石毅与合04-29

-
北京海基科技发展有限公司 21178

-
北京航空航天学会 21428

-
南京工业大学 8274

-
FEAFEWA 24855

-
中国材料研究会 21460

-
吉林小松工程机械有限公司 24396

-
深圳鸿丰大酒店 18317

-
中国科学技术大学 2487

-
杭州爱丁堡酒店 18521

-
北京电子学会 21887

-
香港科学与工程研究中心 23350

-
华中师范大学 24373

-
北京颜路医学科技有限公司 8229

-
北京大学政治发展与政府管理研究中 23399

-
水利技术中心 23365

-
东都国际展览(北京)有限公司 8184

-
贵州大学 23698

-
北京农业工程学会 18424

-
2018年经济管理与绿色发展国际 23278

-
中国科学院广州地球化学研究所 21237























 167
167