我国学者在合成生物基因调控序列智能设计领域取得进展
2025/06/03
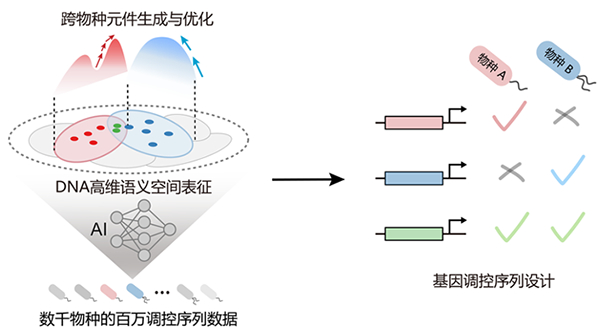
图1 跨物种基因调控序列的逆向设计
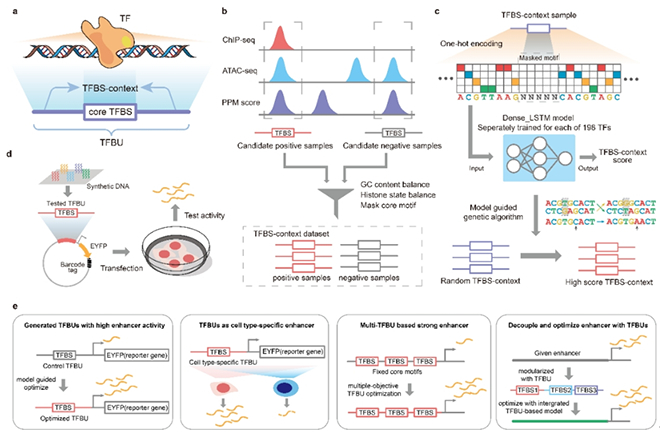
图2 基于TFBU的增强子模块化建模与智能设计
在国家自然科学基金项目(批准号:62250007、62225307)等资助下,清华大学自动化系汪小我教授团队在合成生物基因调控序列智能设计取得进展,系列研究成果连续发表两篇论文:(1)以“系统表示与优化实现细菌跨物种调控序列的逆向设计(Systematic representation and optimization enable the inverse design of cross-species regulatory sequences in bacteria)”为题,于2025年2月19日发表于《自然•通讯》(Nature Communications)期刊上。论文链接:https://doi.org/10.1038/s41467-025-57031-1;(2)以“通过引入和利用转录因子结合单元对增强子进行建模和设计(Modeling and designing enhancers by introducing and harnessing transcription factor binding units)”为题,于2025年2月8日发表于《自然•通讯》(Nature Communications)期刊上。论文链接:https://www.nature.com/articles/s41467-025-56749-2。
针对生物制造中基因线路跨宿主适配性差的瓶颈问题,研究团队从信息编码角度出发,将功能调控序列表征为DNA序列空间中的条件概率分布,发现跨物种调控规律隐含于不同物种条件概率分布的交叠区域;通过整合数千物种的百万级功能序列数据,构建了跨越物种边界的DNA高维语义表征空间和智能生成模型,突破了天然元件的物种屏障,实验结果表明:该模型在大肠杆菌和铜绿假单胞菌中实现了93.3%的跨宿主序列适配准确率(图1)。此外,针对哺乳动物细胞基因增强子定量建模难题,提出了一种新的转录因子结合单元(TFBU)模型;该模型将转录因子的核心结合位点与其周围环境序列作为一个功能整体进行建模,突破了传统方法仅关注结合位点局部组合、忽视序列上下文全局效应的局限,成功量化了环境序列对转录因子结合和增强子活性的影响,为基因治疗等新型疗法开发提供了新的工具(图2)。
系列研究将智能模型驱动的数字进化与主动学习驱动的合成生物实验相结合,通过“虚拟世界”与“物质世界”的协同探索和闭环迭代优化,显著提升了合成生物序列的设计效率。
文章来源国家自然科学基金委员会,分享只为学术交流,如涉及侵权问题请联系我们,我们将及时修改或删除。
-
2025年通信网络与智能系统工程国际 07-14

-
2025年8月优质学术会议推荐 346

-
2025年第十二届能源与环境研究国际 315

-
2025年机械工程,新能源与电气技术 499

-
2025年计算机科学、图像分析与信号 472

-
2025年材料化学与燃料电池技术国际 422

-
2025年第四届国际生物医药产业发展 07-23

-
2025年可持续能源、热力学与机械工 07-23

-
2025年量子计算、算法优化与计算理 07-23

-
2025年航空航天技术、智能导航与无 07-23

-
2025年人工智能、大数据与高性能计 07-23

-
2025年机器学习、计算机视觉与智能 07-23

-
2025年心理健康、社会行为与教育国 07-23

-
2025年戏剧影视、艺术美学与文化国 07-23

-
2025年教育创新与人文艺术国际会议 07-23

-
2025最新JCR分区及影响因子1694

-
好学术:科研网址导航|学术头条分399

-
《时代技术》投稿全攻略:一位审稿408

-
2025年国际期刊预警名单发布!535

-
2025年中科院期刊分区表重磅发3794

-
中科院已正式发布2024年预警期793

-
2025年度国家自然科学基金项目673

-
中国科协《重要学术会议目录(202501

-
2024年国家自然科学基金项目评1064

-
2024年JCR影响因子正式发布1143

-
吉林大学校长张希:学术会议中的提1312

-
分享几种信息检索的方法,高效获取07-23

-
EI检索索引:类型分享,优化你的07-23

-
计算机领域文献的Ei检索:流程详07-23

-
EI检索参考,文献问题分析07-23

-
WILL 23990

-
西安电子科技大学 23092

-
星界会务服务(深圳)有限公司 8151

-
电子科技大学 22995

-
GEAT 7850

-
河北承德盛世会议服务有限公司 22927

-
东南大学数学系 18075

-
医学会议在线 21388

-
唐山创新会议服务有限公司 23919

-
广州市佰特会展有限公司 21137

-
博锐国际展览有限公司 24013

-
国际工学技术出版协会 23028

-
MHDT 8286

-
宁波包豪斯创意文化策划有限公司 22846

-
三盛励展 1958

-
HKSME 24155

-
广州市锐博生物科技有限公司 2009

-
中国能源学会 17970

-
中国兵工学会 21118

-
国防科技大学计算机学院 21136



















 88
88