中国科学院化学研究所在基于纳米孔技术的多肽测序方面取得进展
2024/03/28
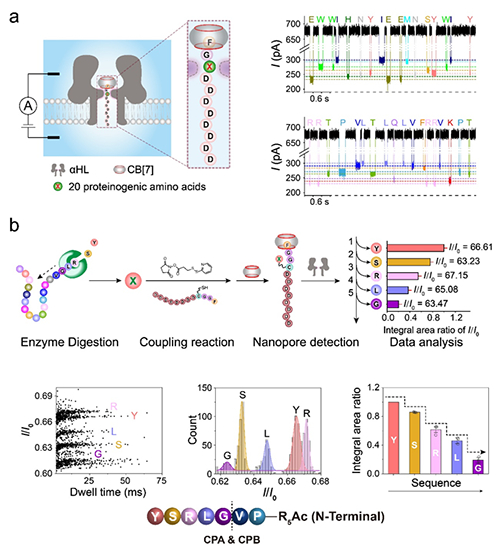 |
图 (a) α-溶血素纳米孔对20种氨基酸的高精度分辨;(b) 基于纳米孔技术的多肽测序
在国家自然科学基金项目(批准号:22025407、21974144)等资助下,中国科学院化学研究所吴海臣研究员团队在基于纳米孔技术的多肽测序方面取得进展。相关研究成果以“基于主客体相互作用的纳米孔多肽测序(Peptide sequencing based on host–guestinteraction-assisted nanopore sensing)”为题,于2023年11月14日发表在《自然•方法》(Nature Methods)。论文链接:https://doi.org/10.1038/s41592-023-02095-4。
蛋白质由氨基酸长链组成,其序列由其基因的核苷酸序列决定。然而,基因序列并不直接编码蛋白质丰度、翻译后修饰或剪接等信息。因此,发展高效、低成本的蛋白质测序和翻译后修饰鉴定策略对于蛋白质组学研究非常必要。目前蛋白质测序的主流方法是Edman降解和质谱法,这两种方法无论在测序长度、检测灵敏度、准确性,或者通量和价格上都存在局限性。因此,近年来科学家们积极发展新的蛋白质测序方法,包括单分子荧光方法、隧穿电流技术和纳米孔技术,但尚未能真正实现蛋白质的从头测序。
该团队研究发现,N端为苯丙氨酸的多肽与胍环分子结合后,增加了多肽穿孔的阻滞时间,使α-溶血素纳米孔对其N端第3位点具有超高的分辨率,可对20种氨基酸进行有效区分。实现蛋白质测序最关键的步骤是获得氨基酸的序列信息。研究人员利用羧肽酶A和羧肽酶B将肽段中的氨基酸逐一水解,并将游离的氨基酸通过偶联反应连接到N端为苯丙氨酸、C端为8个天冬氨酸的多肽探针上,最后通过纳米孔单通道的电流信号确定每个氨基酸的种类,利用其信号丰度确定序列位置,从而成功实现了基于纳米孔技术的多肽序列测定。
文章来源国家自然科学基金委员会,分享只为学术交流,如涉及侵权问题请联系我们,我们将及时修改或删除。
-
2026年6月优质国际学术会议推荐 7

-
2026年第17届机械与航空航天工程 193

-
2026年先进航空航天技术与卫星应用 324

-
2026资源、化学化工与应用材料国际 1808

-
2026年图像处理与数字创意设计国际 1632

-
2026年机械工程,新能源与电气技术 6095

-
2026年材料科学、低碳技术与动力工 1819

-
2026年艺术、文化产业与数字媒体国 04-29

-
2026年智慧教育、教育研究与文化交 04-29

-
2026年数字社会、公共管理与经济学 04-29

-
2026 政务服务、数字治理与智慧城 04-28

-
2026 制冷技术、暖通设备与环境调 04-28

-
2026 轻工材料、绿色制造与循环利 04-28

-
2026 多语言智能、翻译技术与国际 04-28

-
2026 生物育种、生态种植与现代农 04-28

-
中国科协发布2025年《重要学术12

-
2026年新锐分区(原中科院期刊2595

-
2025年两院院士增选有效候选人4402

-
2025最新JCR分区及影响因子12342

-
好学术:科研网址导航|学术头条分5673

-
2025年国际期刊预警名单发布!5837

-
2025年中科院期刊分区表重磅发20812

-
吉林大学校长张希:学术会议中的提6954

-
二维超导迈斯纳效应探测研究获进展04-29

-
研究发现笼目超导体中多重范霍夫奇04-29

-
二氧化碳加氢制高碳烯烃与航煤馏分04-29

-
靶向特定蛋白互作界面抑制乙肝病毒04-29

-
研究揭示内源信使调控膜损伤与细胞04-29

-
科学家绘制大脑星形胶质细胞转录因04-29

-
上海交大Bio-X研究院石毅与合04-29

-
南京大陆产业 21278

-
广州市香港科大霍英东研究院 24238

-
固体废物管理与技术国际会议 18413

-
浙江理工大学 23396

-
世界汉语教学学会 18487

-
福建省空间信息中心 21406

-
京师博仁(北京)教育科技中心 21490

-
中国化工学会培训中心 2339

-
哈尔滨同泰会议服务有限公司 18197

-
福建志联会展有限公司 8337

-
重庆交通大学管理学院 21384

-
仁济医院信息中心 21414

-
北京太阳花酒店 2199

-
武汉奔诚文化传播有限公司 8298

-
武汉华联帕博文化传播有限公司 23499

-
武汉青博盛学术服务有限公司 2290

-
上海易标科技 18712

-
上海电子信息职业技术学院 23257

-
闪耀科技(深圳)有限公司 18501

-
香港国际学术研究协会 25318























 803
803